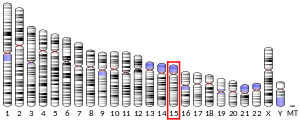
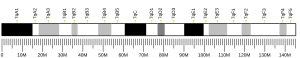
CHD2 - CHD2
A proteína 2 de ligação de cromodomínio -helicase-DNA é uma enzima que, em humanos, é codificada pelo gene CHD2 .
Função
A família de proteínas CHD é caracterizada pela presença de domínios cromo (modificador da organização da cromatina) e domínios de helicase / ATPase relacionados com SNF2 . Os genes CHD alteram a expressão gênica, possivelmente pela modificação da estrutura da cromatina , alterando assim o acesso do aparelho de transcrição ao seu molde de DNA cromossômico. CHD2 catalisa a montagem da cromatina em arranjos periódicos; e a região N-terminal de CHD2, que contém cromodomínios em tandem, tem um papel auto-inibitório nas atividades de ligação ao DNA e ATPase de CHD2. Variantes transcritas em splicing alternativo que codificam isoformas distintas foram encontradas para este gene.
Significado clínico
Mutações e deleções de novo neste gene foram associadas a casos de encefalopatias epilépticas.
A epilepsia CHD2 está cada vez mais sendo identificada como uma subpopulação da Síndrome de Lennox-Gastaut .
A encefalopatia mioclônica CHD2 é uma condição caracterizada por convulsões recorrentes (epilepsia), função cerebral anormal (encefalopatia) e deficiência intelectual. A epilepsia começa na infância, geralmente entre 6 meses e 4 anos. Cada indivíduo pode apresentar vários tipos de convulsões, mais comumente convulsões mioclônicas.
Recentemente, mutações ou deleções de novo em CHD2 foram associadas à deficiência intelectual e ao autismo. Os pesquisadores descobriram 27 genes que abolem a função da proteína correspondente - em pelo menos duas pessoas com autismo, e 6 genes são mutados em três ou mais pessoas com autismo. Esses seis genes - CHD8 , DYRK1A , ANK2 , GRIN2B , DSCAM e CHD2 - são os candidatos mais fortes ao autismo identificados até agora.
Apoio da família
As síndromes associadas a mutações ou deleções em CHD2 podem ser devastadoras. Famílias de indivíduos com mutações ou deleções em CHD2 podem se juntar a um grupo de pesquisa e apoio.
Referências
Leitura adicional
- Feys T, Poppe B, De Preter K, Van Roy N, Verhasselt B, De Paepe P, De Paepe A, Speleman F (julho de 2007). "Um inventário detalhado das alterações do número de cópias do DNA em quatro linhas de células de linfoma de Hodgkin comumente usadas" . Haematologica . 92 (7): 913–20. doi : 10.3324 / hematol.11073 . PMID 17606441 .
- Kimura K, Wakamatsu A, Suzuki Y, Ota T, Nishikawa T, Yamashita R, Yamamoto J, Sekine M, Tsuritani K, Wakaguri H, Ishii S, Sugiyama T, Saito K, Isono Y, Irie R, Kushida N, Yoneyama T , Otsuka R, Kanda K, Yokoi T, Kondo H, Wagatsuma M, Murakawa K, Ishida S, Ishibashi T, Takahashi-Fujii A, Tanase T, Nagai K, Kikuchi H, Nakai K, Isogai T, Sugano S (janeiro de 2006 ) "Diversificação da modulação transcricional: identificação em larga escala e caracterização de promotores alternativos putativos de genes humanos" . Genome Research . 16 (1): 55–65. doi : 10.1101 / gr.4039406 . PMC 1356129 . PMID 16344560 .
- Hiller M., Huse K., Platzer M., Backofen R. (2005). "Predição não baseada em EST de eventos de salto de exon e retenção de íntron usando informações Pfam" . Nucleic Acids Research . 33 (17): 5611–21. doi : 10.1093 / nar / gki870 . PMC 1243800 . PMID 16204458 .
- Brandenberger R, Wei H, Zhang S, Lei S, Murage J, Fisk GJ, Li Y, Xu C, Fang R, Guegler K, Rao MS, Mandalam R, Lebkowski J, Stanton LW (junho de 2004). "A caracterização do transcriptoma elucida redes de sinalização que controlam o crescimento e a diferenciação das células ES humanas". Nature Biotechnology . 22 (6): 707–16. doi : 10.1038 / nbt971 . PMID 15146197 . S2CID 27764390 .
- Johnson JM, Castle J, Garrett-Engele P, Kan Z, Loerch PM, Armor CD, Santos R, Schadt EE, Stoughton R, Shoemaker DD (dezembro de 2003). "Pesquisa de todo o genoma de splicing pré-mRNA alternativo humano com microarrays de junção de exon". Ciência . 302 (5653): 2141–4. Bibcode : 2003Sci ... 302.2141J . doi : 10.1126 / science.1090100 . PMID 14684825 . S2CID 10007258 .
links externos
- FactorBook CHD2
- Localização do genoma humano CHD2 e página de detalhes do gene CHD2 no navegador do genoma UCSC .